使用kmplot在线进行生存分析
- 2019 年 12 月 19 日
- 筆記
kmplot是一个生存分析的在线工具,最初是设计用来对肝癌中的miRNA进行生存分析,对应的文章发表在scientific reports上,链接如下
https://www.nature.com/articles/s41598-018-27521-y.pdf
数据库构建的过程如下

从TCGA, GEO等大型数据库中收集肝癌相关的miRNA表达谱数据,同时从文献中整理已报到的生存相关biomarker miRNA进行生存分析,综合cox回归和差异表达的结果,进一步筛选biomarker miRNA。
后来在此基础上进一步拓展, 目前支持21种肿瘤类型,包括miRNA和mRNA的生存分析,网址如下
http://kmplot.com/analysis/
用法也非常简单,以乳腺癌为例,点击首页对应的菜单进入对应的分析页面

1. 输入感兴趣的基因
支持探针ID或者gene symbol, 会有对应的提示框,这里以tp53为例,如下图所示

也可以通过use multiple genes, 输入多个基因,批量进行生存分析
2. 确定样本分组策略
根据基因表达量将样本分成高低两组,这里支持按照均值等多种统计量来分类,示意如下

3. 确定生存分析的类型
支持多种事件的生存分析,对应不同的类型,示意如下
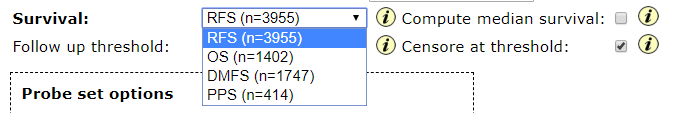
RFS对应relapse free survival,以复发作为生存分析中的事件,用来分析手术治疗的效果,RFS的具体解释参见以下链接
https://www.cancer.gov/publications/dictionaries/cancer-terms/def/rfs
OS代表Overall survival,分析从确诊开始之后患者的生存时间,OS的具体解释参见以下链接
https://www.cancer.gov/publications/dictionaries/cancer-terms/def/os
DMFS代表Distant Metastasis Free survival, 将肿瘤的转移作为生存分析中的事件;PPS代笔post progression survival, 主要分析预后的生存情况。
4. 筛选样本
可以根据临床信息等指标筛选样本,当然这一步是可选的,示意如下

确定好之后,直接点击Draw Kaplan-Meier plot即可,结果如下所示



